เทคโนโลยีการแก้ไขหรือเปลี่ยนแปลงลำดับเบสของ DNA ในเซลล์หรือ Gene editing ในปัจจุบันสามารถใช้ในการศึกษาเพื่อตรวจวินิจฉัยโรค หรือการรักษาโรคที่เกี่ยวกับการกลายพันธุ์ของมนุษย์ได้ นอกจากนี้ยังสามารถดัดแปลงพันธุกรรมของพืชหรือสัตว์เพื่อให้ได้ผลผลิตหรือลักษณะที่ต้องการ ซึ่งการทำ gene editing มีหลายเทคนิคด้วยกัน ได้แก่ TALEN, ZFNs และCRISPR-Cas9 เป็นต้น
โดย CRISPR-Cas9 เป็นเทคโนโลยีที่ได้รับความสนใจอย่างมากในช่วงๆที่ผ่านมา โดยเทคโนโลยีนี้ใช้ guide-RNA เป็นเหมือนตัวแม่พิมพ์ที่เอาไว้ใช้ระบุตำแหน่งของ target-DNA จากนั้นจะถูกตัดให้ขาด โดยโปรตีน cas9 เพื่อเปลี่ยนแปลงหรือแก้ไขลำดับเบส ของ DNA ซึ่งทำให้สามารถแก้ไขหรือปรับปรุงพันธุกรรมของสิ่งมีชีวิตได้อย่างมีประสิทธิภาพ ซึ่งสามารถนำมาประยุกต์กับงานวิจัยหลายด้าน เช่น เซลล์บำบัด งานต้านไวรัสและเชื้อจุลชีพ งานด้านเกษตร การประยุกต์ใช้ทางเทคโนโลยีชีวภาพอาหารและอุตสาหกรรม เป็นต้น
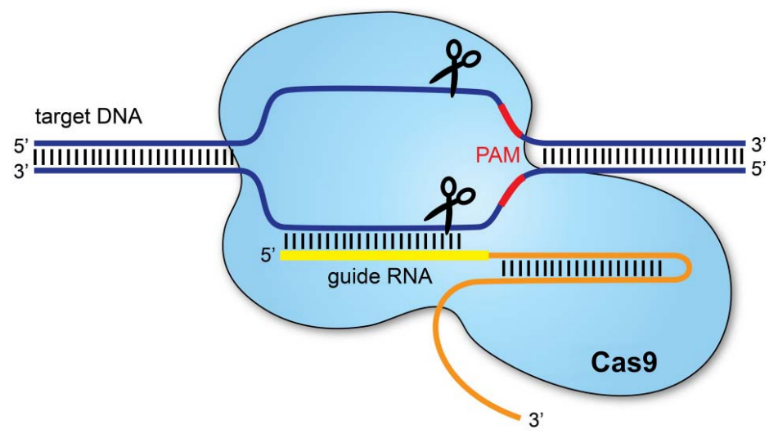
ภาพที่ 1 ระบบการทำงานของ Crispr-cas9 (source: Redman et al., 2016)
สำหรับผลการศึกษา Gene editing ด้วยเทคนิค CRISPR-Cas9 สามารถตรวจสอบผลได้หลายวิธี ตัวอย่างเช่น
- Gel electrophoresis: วิธีนี้เป็นการศึกษาขนาดของดีเอ็นเอที่ผ่านการแก้ไขแล้วเมื่อเทียบกับตัวอย่างที่ยังไม่ได้แก้ไข เพื่อระบุมีว่าการแก้ไขยีนได้ผล
- Restriction Fragment Length Polymorphism (RFLP) (RFLP): เป็นการตรวจสอบความแตกต่างหรือการเปลี่ยนแปลงของชิ้น DNA หลังจากถูกย่อยด้วยเอนไซม์ตัดจำเพาะ
- High-resolution melt analysis: สามารถตรวจหาการเปลี่ยนแปลงลำดับเบสของ DNA ผ่านการหา Melting temperature ในขั้นตอนของการทำ real-time PCR
- Sequencing: สามารถใช้เพื่อยืนยันการเกิด editing ของยีนที่ต้องการ โดยลำดับเบสของ DNA ที่ถูกแก้ไขจะถูกเปรียบเทียบกับกับลำดับเบสของ DNA ที่ไม่ถูกแก้ไข เพื่อดูการเปลี่ยนแปลงที่เกิดขึ้น
ซึ่งการวัดผลด้วยวิธีการเหล่านี้ บางวิธีอาจจะเกิด False positive ได้ง่าย หรือในบางวิธีอาจจะมีค่าใช้จ่ายในการวิเคราะห์สูง ดังนั้นจึงได้มีการนำเทคนิค Digital PCR เข้ามาใช้ช่วยเพิ่มประสิทธิภาพในการตรวจสอบ
QIAcuity เป็นเครื่อง Digital PCR ใช้หลักการ Nanoplate-Based Partition Digital PCR ซึ่งเป็นเทคโนโลยีการทำ PCR ที่ใช้หลักการการแบ่ง PCR reaction ออกเป็น reaction ย่อยๆ เพื่อใช้ในการศึกษาหาปริมาณของสารพันธุกรรมที่สนใจ (Absolute quantification) โดยที่ผู้ใช้งานไม่จำเป็นต้องสร้าง Standard Curve ซึ่งเครื่องจะทำการวัดผลการทำปฏิกิยาที่เกิดขึ้นจากสัญญาณฟลูออเรสเซนต์ ในรูปแบบ positive และ negative partition จากนั้นนำผลที่ได้มาคำนวณหาปริมาณสารพันธุกรรมต่อไป โดยเครื่อง QIAcuity รองรับการอ่านสัญญาณฟลูออเรสเซนต์ทั้ง ระบบ Intercalating Dye และ Probe และยังรับการทำ Multiplex ได้สูงสุด 5 ช่องสี

.png)
ซึ่งเทคนิค Digital PCR สามารถเข้ามาเพิ่มประสิทธิภาพการตรวจสอบผลการทำ Gene editing โดย
- ลดการเกิด False positive: ด้วยเทคนิคการทำ partitioning ของ Digital PCR ด้วยการแบ่ง 1 ปฏิกิริยา ออกเป็นหลายหมื่นปฏิกิริยาย่อย ซึ่งจะช่วยลดสัดส่วนระหว่าง inhibitor หรือ non-target DNA ต่อ target DND ลง จึงช่วยลดการเกิด False positive และเพิ่มประสิทธิภาพในการตรวจหาได้
- สามารถตรวจวัดได้อย่างจำเพาะ โดยสามารถตรวจหาการเปลี่ยนแปลงของ DNA แม้จะมีการเปลี่ยนเพียงไม่กี่เบส ก็สามารถจำแนกความแตกต่างในแต่ละกลุ่มประชากรได้
- การวิเคราะห์เชิงปริมาณ: สามารถใช้ Digital PCR ในการช่วยหาปริมาณ target DNA (copy/µl) และ % editing fragment ของตัวอย่างได้
ดังนั้นแล้ว Digital PCR จึงเป็นอีกวิธีหนึ่งที่สามารถใช้ตรวจสอบการทำ Gene editing ด้วย CRISPR-Cas9 ได้อย่างมีประสิทธิภาพ โดยสามารถลดการเกิดผล False negative สามารถตรวจวัดได้อย่างจำเพาะได้ และยังช่วยวิเคราะห์หาปริมาณสารพันธุกรรมแบบ Absolute quantification ของตัวอย่างได้อีกด้วย เพื่อให้ผู้วิจัยได้รับผลการทดลองที่ถูกต้องและแม่นยำสูงสุด
โดยการศึกษางาน Gene editing ด้วยเครื่อง QIAcuity สามารถใช้ร่วมกับน้ำยา QIAcuity Probe PCR Kit สำหรับการตรวจสอบด้วยระบบ Probe หรือ QIAcuity EG PCR Kit เมื่อต้องการตรวจสอบด้วยระบบสี Intercalating dye และหากต้องการการศึกษางานทางด้าน Cell and Gene therapy ทาง QIAgen ยังมีผลิตภัณฑ์ที่รองรับงานทางด้านนี้โดยเฉพาะ ไม่ว่าจะเป็นชุดน้ำยา QIAcuity Residual DNA Quantification Kits เพื่อใช้ดูการปนเปื้อนของ DNA จาก Host cell ไม่ว่าจะเป็นชนิด HEK 293 cell, CHO cell และ E.coli นอกจากนี้ยังมีชุด dPCR CGT Assay ที่ใช้ในการตรวจสอบการเปื้อนของ Adeno-associated virus vector (AAV) ในตัวอย่างที่ทำการผลิตออกมาได้ด้วยเช่นกัน
|
|
QIAcuity Probe PCR Kit (1 ml)
|
Cat. No. 250101
|
|
|
QIAcuity EG PCR Kit (1 ml)
|
Cat. No. 250111
|
|
|
QIAcuity HEK293 resDNA Quant Kit (96) QIAcuity CHO resDNA Quant Kit (96) QIAcuity E. coli resDNA Quant Kit (96) |
Cat. No. 250224 Cat. No. 250222 Cat. No. 250220 |
|
|
dPCR CGT Assay
|
Cat. No. 250230
|
References
Barrangou, R., & Doudna, J. A. (2016). Applications of CRISPR technologies in research and beyond. Nature biotechnology, 34(9), 933-941.
Carroll, D. (2014). Genome engineering with zinc-finger nucleases. Genetics, 188(4), 773-782.
Doudna, J. A., & Charpentier, E. (2014). Genome editing. The Science of Life: Projects and Principles for Beginning Biologists, 1.
Gaj, T., Gersbach, C. A., & Barbas III, C. F. (2013). ZFN, TALEN, and CRISPR/Cas-based methods for genome engineering. Trends in biotechnology, 31(7), 397-405.
Huggett, J. F., & Whale, A. (2017). Digital PCR as a novel technology and its potential implications for molecular diagnostics. Clinical Chemistry, 63(12), 1782-1793.
Jinek, M., Chylinski, K., Fonfara, I., Hauer, M., Doudna, J. A., & Charpentier, E. (2012). A programmable dual-RNA–guided DNA endonuclease in adaptive bacterial immunity. Science, 337(6096), 816-821.
Komor, A. C., Kim, Y. B., Packer, M. S., Zuris, J. A., & Liu, D. R. (2016). Programmable editing of a target base in genomic DNA without double-stranded DNA cleavage. Nature, 533(7603), 420-424.
Redman, M., King, A., Watson, C., & King, D. (2016). What is CRISPR/Cas9?. Archives of Disease in Childhood-Education and Practice, 101(4), 213-215.
สนใจสอบถามรายละเอียดเพิ่มเติมได้ที่
หรือติดต่อ Info@biodesign.co.th หรือ Line: @BioDesign หรือ https://www.facebook.com/BioDesignTH
“บทความผลิตภัณฑ์โดย คุณอัจฉริยา พรหมจรรยา Product Specialist บริษัท ไบโอดีไซน์ จำกัด”
.jpg)
(1).jpg)
.png)